标题: Genome and transcriptome-wide analyses identify multiple candidate genes and a significant polygenic contribution in bicuspid aortic valve
期刊:Circulation
部分名词对照
论文专有名词对照表
| 术语缩写 | 英文全称 | 中文含义与在文中的作用 |
|---|---|---|
| GWAS | Genome-Wide Association Study | 全基因组关联分析:通过扫描大量个体的基因组,寻找与疾病(如 BAV)相关的常见遗传变异。 |
| TWAS | Transcriptome-Wide Association Study | 全转录组关联分析:结合基因表达数据和 GWAS 结果,识别表达水平与疾病相关的基因。 |
| PRS | Polygenic Risk Score | 多基因风险评分:汇总多个微小影响的遗传变异得分,用以预测个体患病的风险。 |
| eQTL | Expression Quantitative Trait Locus | 表达定量性状位点:指基因组上能够影响基因表达水平的特定区域。 |
| LD | Linkage Disequilibrium | 连锁不平衡:指不同位点上的等位基因非随机共同遗传的现象,用于精细定位致病变异。 |
| MR | Mendelian Randomization | 孟德尔随机化:一种统计方法,利用遗传变异作为“工具变量”来评估基因表达与疾病之间的因果关系。 |
| COLOC | Bayesian Colocalization | 贝叶斯共定位分析:评估 GWAS 信号与 eQTL 信号是否由同一个遗传变异引起,以增加证据可信度。 |
| FDR | False Discovery Rate | 错误发现率:一种统计校正方法,用于在进行大量平行测试时控制假阳性的比例。 |
| OR | Odds Ratio | 比值比:衡量某种遗传变异与疾病关联强度的指标;OR > 1 表示该变异会增加患病风险。 |
| SNP | Single Nucleotide Polymorphism | 单核苷酸多态性:基因组中单个碱基的变异,是 GWAS 研究中最常见的遗传变异类型。 |
| GTEx | Genotype-Tissue Expression | 基因型-组织表达项目:一个大型公共数据库,提供人体各组织中的基因表达和遗传调控信息。 |
| PCW | Postconception Week | 受孕后周数:用于标记人类胎儿组织样本的发育阶段(如 9-20 PCW)。 |
| dpf | Day Postfertilization | 受精后天数:用于描述斑马鱼胚胎的发育年龄。 |
| MO | Morpholino Oligonucleotide | 吗啉基反义寡核苷酸:一种用于暂时降低(敲降)斑马鱼特定基因表达的实验技术。 |
引言
为什么值得研究?核心矛盾——“遗传性很强,但机制解释不足”
BAV 是最常见先天性心脏缺陷之一(约0.5%–1%)。
与主动脉病变、CAVS、瓣膜返流等并发症相关,且中长期负担重。
BAV 遗传度高家族聚集明显,但已知单基因突变/综合征只能解释少数病例。
研究空白:从“少数基因”转向“多基因架构”
- 既往 GWAS 仅报告有限位点(如 GATA4/PALMD/TEX41/MUC4 相关区域)。对比的是最新的23年发表于EHJ的meta分析,供参考:Bray, J. J. H., Freer, R., Pitcher, A. & Kharbanda, R. Family screening for bicuspid aortic valve and aortic dilatation: A meta-analysis. Eur. Heart J. 44, 3152–3164 (2023).
- 作者指出仍不足以解释绝大多数BAV。
研究目标:规模化发现 + 机制优先化 + 风险转化
本研究目标不是单一层面,而是:
- 更大样本GWAS发现位点;
- 结合主动脉瓣组织转录组优先化候选因果基因;
- 用斑马鱼做发育功能验证;
- 构建PRS评估临床相关性。
结果部分
识别 BAV 的基因组位点 (GWAS Meta-analysis)
- 研究方法:研究人员对来自欧洲和北美的 17 个研究(包含 9,631 名 BAV 患者和 56,046 名对照者)进行了全基因组关联分析(GWAS)元分析。他们使用了固定效应元分析方法,并利用 FinnGen、All of Us 和 UK Biobank 等大型队列进行了验证。
- 研究结果:共识别出 36 个达到全基因组显著水平的位点(P<5×10−8),其中 32 个是首次发现的新位点。SNP 遗传率估计在责任量表上为 11.7%。
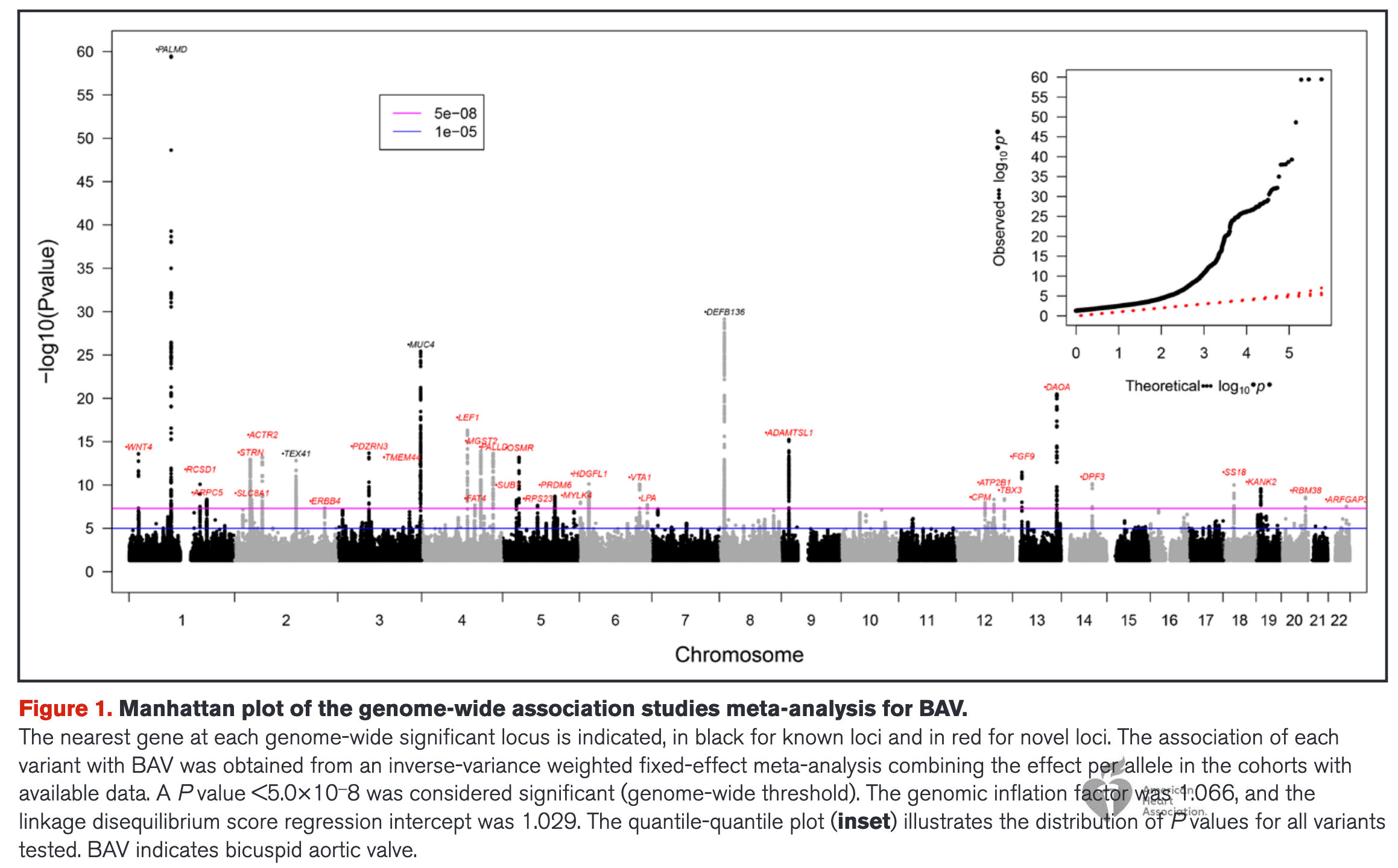
补充学习:曼哈顿图 (Manhattan Plot) 的阅读方法,曼哈顿图得名于其外形像曼哈顿的天际线,图中的每一个“点”代表一个遗传变异位点(SNP)。
横轴 (X-axis) – 染色体 (Chromosome) :显示了人类的 1 到 22 号常染色体。点在横轴上的位置代表该变异在基因组中的物理位置。
纵轴 (Y-axis) – 显著性 ( −log10P-value ) :代表关联的统计显著性。数值越高,表示该变异与 BAV 的关联越不可能由于偶然产生。
显著性阈值线:
- 粉色横线:代表全基因组显著性阈值 ( 5×10−8 ) 。任何超过这条线的“塔尖”都被认为是与疾病真正相关的遗传位点。
- 蓝色横线:通常代表暗示性显著水平 (1×10−5)。
标签与颜色:
- 图中上方标注了各个位点附近的基因名称。
- 红色字体:代表本次研究中首次发现的新位点(共 32 个)。
- 黑色字体:代表之前研究已经报道过的已知位点(如 PALMD, GATA4 等)。
- 最高的点 (PALMD) :这代表了全基因组中关联信号最强的区域。
补充学习:QQ 图 (Figure1中右上角插图) 的阅读方法,QQ 图用于评估研究结果的整体可靠性,判断是否存在统计偏差(如群体分层)。
红虚线:代表“无效假设”的情况,即如果基因变异与疾病完全没有关系,所有的点应该分布在这条线上。
黑色实点:代表实际观察到的数值。
如何解读:
- 大部分点在左下角重合,说明模型校正得很好。
- 右上角的“上翘”部分:这是研究者最想看到的,它表示有些位点远远偏离了随机分布,证明这些是真正的遗传关联信号。
指标:图中提到的“基因膨胀系数 (λ)”为 1.066,这说明实验结果受偏差干扰很小,数据非常干净。
转录组关联分析与因果基因优先排序 (TWAS, Colocalization & MR)
研究方法:
- 利用 484 份人类主动脉瓣样本的 RNA 测序数据进行 eQTL 分析。
- 结合 GWAS 结果和瓣膜、主动脉及左心室等组织的表达模型进行全转录组关联分析(TWAS) 。
- 利用 Bayesian 共定位分析 (COLOC) 和孟德尔随机化 (MR) 来评估基因表达水平与 BAV 风险之间的因果关系。
研究结果:在主动脉瓣中识别出 25 个 eQTLs,TWAS 发现 27 个基因的表达与 BAV 显著相关。其中,KANK2 和 ERBB4 在主动脉瓣中被确定为潜在因果基因;PRDM6 和 STRN 分别在主动脉和左心室组织中被优先筛选出来。
- KANK2:作为肌动蛋白聚合调节因子,其表达量降低会影响内皮细胞迁移并显著增加 BAV 风险。
- ERBB4:作为参与心脏胚胎发育和瓣膜生成的跨膜受体蛋白,其在瓣膜中的低表达与 BAV 风险密切相关。
- PRDM6:作为调节血管平滑肌细胞收缩的转录抑制因子,在胎儿主动脉瓣发育的早期阶段发挥关键作用。
- STRN:作为参与细胞骨架组织和粘附的复合物成分,在实验中被证实对心脏流出道瓣膜的正常发育至关重要。
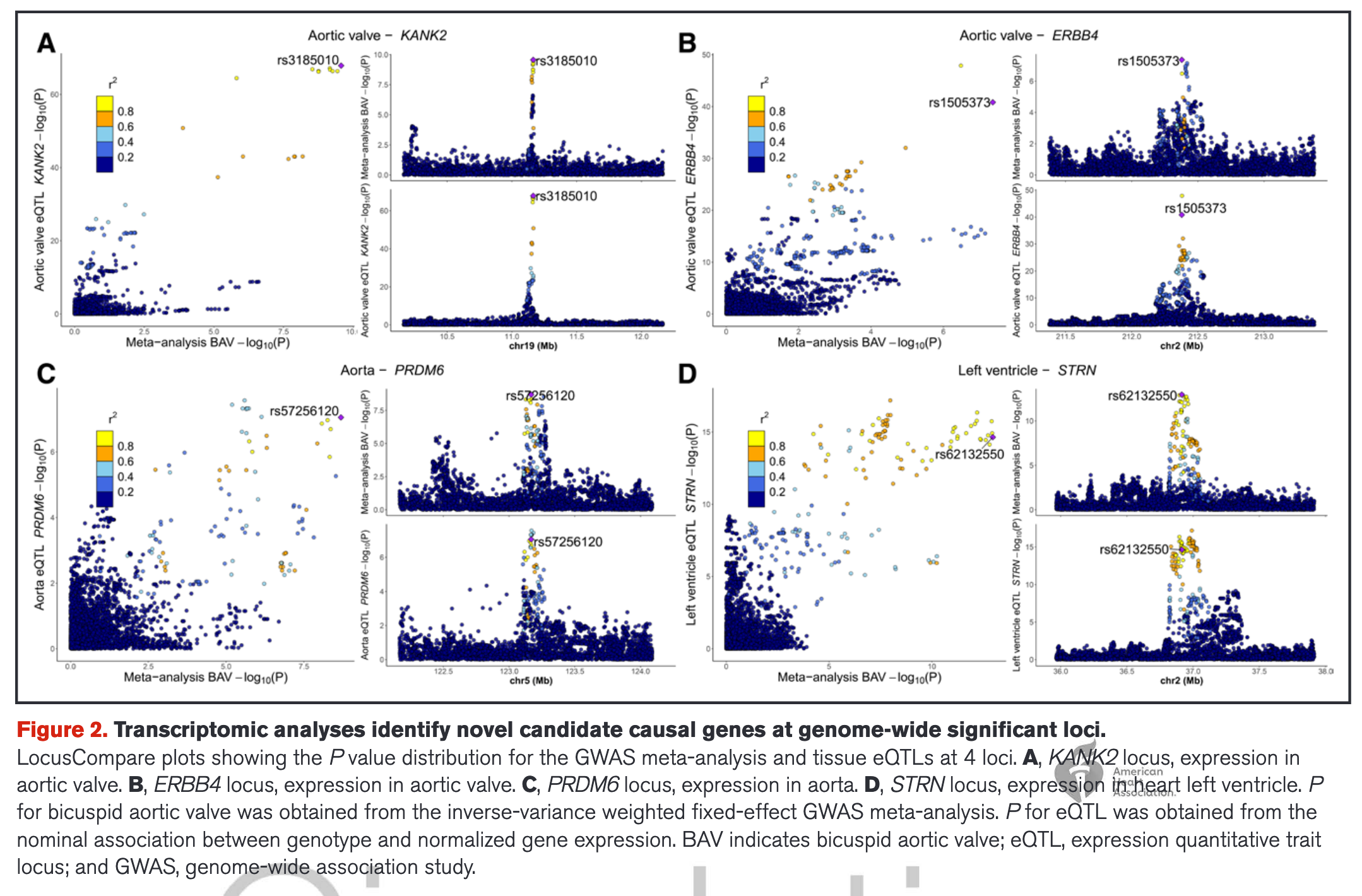
Figure 2 通过 LocusCompare 图展示了这四个核心候选基因在 GWAS 信号与 eQTL 信号之间的共定位情况。
- 布局结构:左图与右图
Figure 2 包含 A、B、C、D 四个面板,分别对应四个关键基因:KANK2、ERBB4、PRDM6 和 STRN。每个面板都由三部分组成:
左侧大的散点图:
- 横轴 (X-axis) :GWAS 的显著性(−log10P),数值越往右,表示与 BAV 关联越强。
- 纵轴 (Y-axis) :eQTL 的显著性(−log10P),数值越往上,表示该位点对基因表达的影响越显著。
右侧两个小的叠加曼哈顿图(局部图) :
- 上方小图:展示 GWAS 在该区域的信号。
- 下方小图:展示 eQTL 在该区域的信号。
- 颜色与符号的含义
紫色菱形点:代表该区域的 Lead SNP(最显著的变异位点) ,并标注了 rsID(如 A 图中的 rs3185010)。
颜色刻度 ( r2 ) :颜色代表其他点与 Lead SNP 的连锁不平衡(LD)强度。
- 红色/橙色:表示与 Lead SNP 高度相关(r2>0.8),它们通常属于同一个遗传“信号团”。
- 蓝色:表示相关性很低。
- 如何判断“关联成功”?
1)左侧图中点的分布:
- 如果大量点(尤其是橙红色的点)分布在右上角,说明这些变异位点既能显著影响疾病风险,也能显著影响基因表达。
- 如果点只分布在横轴或纵轴上,则说明该信号只与其中一项有关,不具备共定位证据。
2)右侧图中“塔尖”的重合度:
- 观察上下两个小图。如果 GWAS 的信号峰(山尖)和 eQTL 的信号峰在水平位置(基因组位置)上完全重叠,且颜色分布一致,说明两者是由同一个遗传变异引起的。
- 实例解读(以 A 图 KANK2 为例)
- 组织:主动脉瓣(Aortic valve)。
- 现象:左图中,rs3185010 位于右上角最显眼的位置;右图中,GWAS 的峰值与 KANK2 的 eQTL 峰值完美对齐。
- 结论:这证明了在主动脉瓣组织中,KANK2 基因表达量的变化是导致 BAV 风险增加的潜在因果机制。
生物通路富集分析
- 研究方法:使用 Metascape 软件对筛选出的 55 个候选基因进行通路富集分析,涵盖 GO 生物过程、KEGG 和 Reactome 等数据库。
- 为什么是55个基因?36 个显著遗传区域(loci) 基于距离+错义变异+eQTL+TWAS+SNP−to−gene的筛选55 个候选基因。这种做法的意义在于,GWAS 只能告诉我们基因组的“哪个地块”有问题,而整合 eQTL 和 TWAS 等证据,能帮研究者指认出到底是这个地块里的“哪一栋房子(基因)”出了故障
- 研究结果:候选基因显著富集在酶联受体蛋白信号通路、管腔形态发生和心脏发育等生物学过程中。
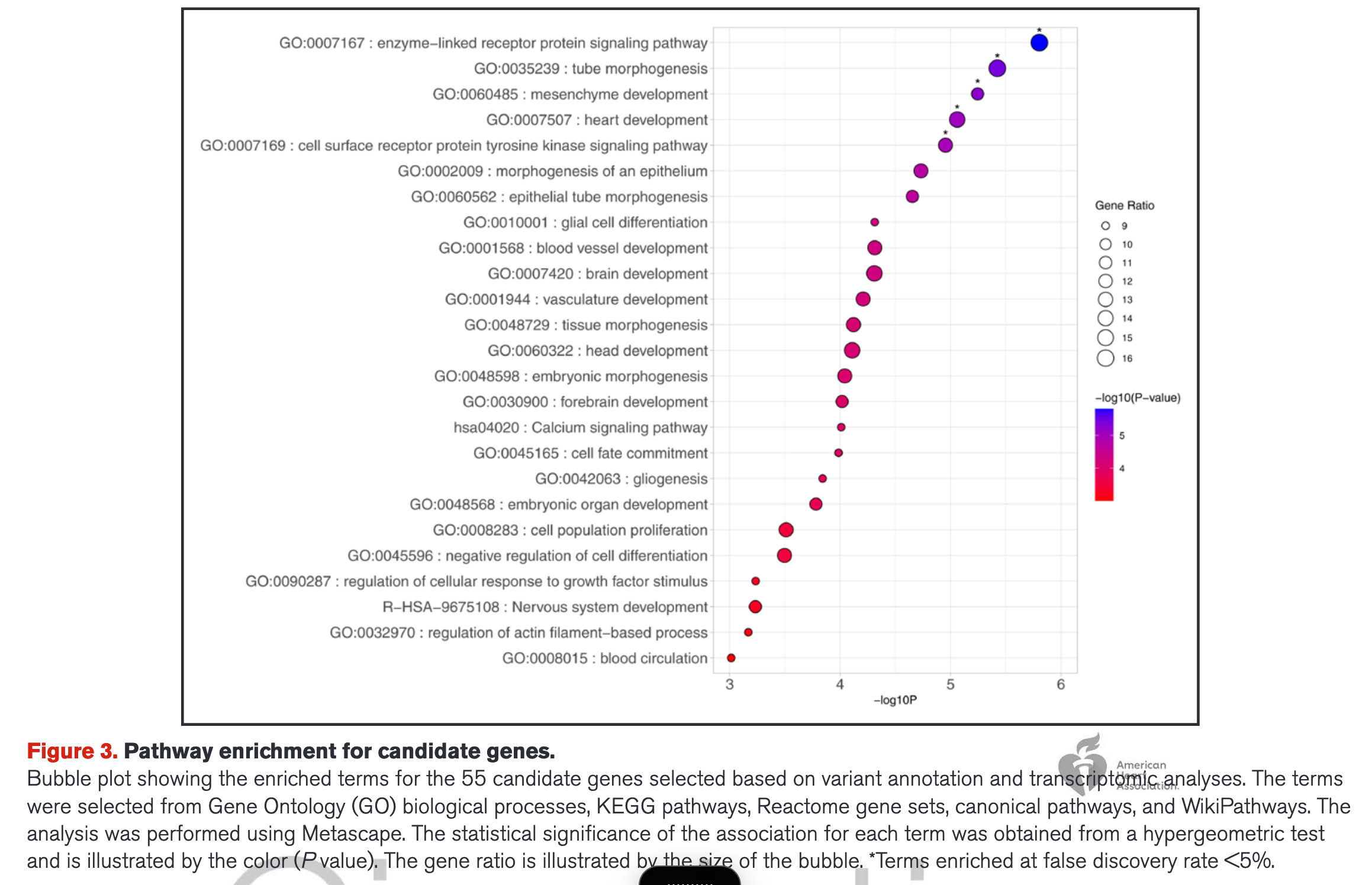
- Figure 3以气泡图的形式展示了显著富集的生物学通路。
候选基因的综合特征评估
- 研究方法:基于 9 项特征(如是否为最近基因、是否有错义变异、eQTL、TWAS、共定位、MR、胎儿瓣膜表达差异、单基因疾病关联等)对候选基因进行打分排序。
- 研究结果:共有 13 个基因拥有 5 个或更多支持特征。得分最高的基因包括 PRDM6、ATP13A3、ERBB4、STRN、KANK2 和 LEF1 等,其中许多参与心脏形态发生。

- Figure 4展示了具有多项证据支持的候选基因综合矩阵图。
斑马鱼体内的功能验证
- 研究方法:选择斑马鱼作为模型,通过 CRISPR/Cas9 介导的基因敲除 (Knockout) 或 Morpholino (MO) 介导的基因敲降 (Knockdown) ,观察其对心脏流出道(OFT)瓣膜发育的影响。使用 双光子显微镜进行活体成像。
- 研究结果:敲降 lef1 或 wnt4 导致 60%-80% 的斑马鱼出现流出道瓣膜畸形。strn 缺失导致瓣膜发育异常及流出道长度缩短;kank2 缺失则导致房室管内皮细胞数量显著增加。
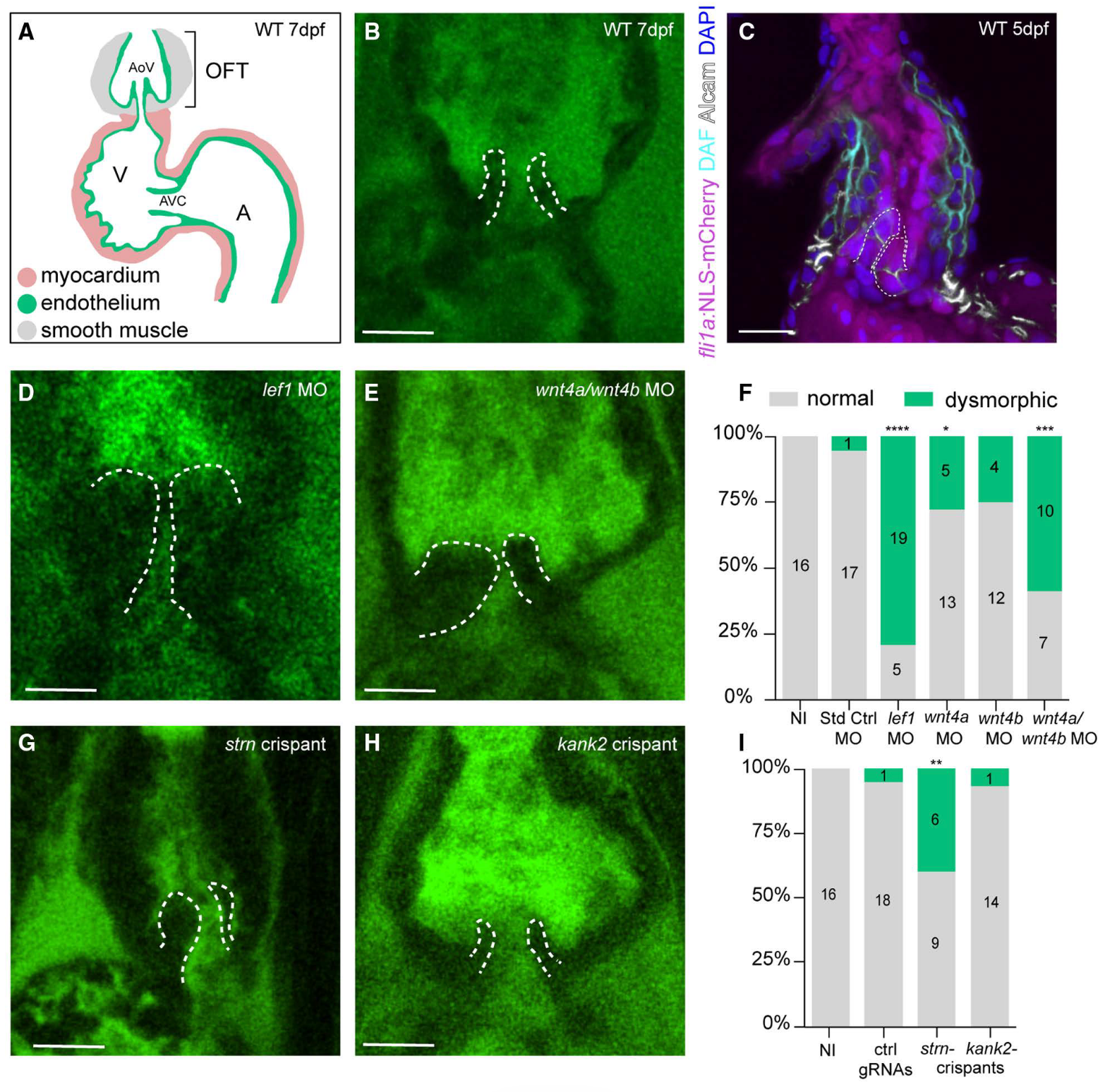
- Figure 5 包含了斑马鱼心脏解剖示意图、荧光成像照片以及瓣膜缺陷的定量统计图。
- 研究使用了名为
Tg(fli1a:NLS-mCherry)ubs10 的转基因斑马鱼系。这一品系能够让斑马鱼的内皮细胞(包括心脏内膜细胞)表达红色荧光蛋白(mCherry),从而在显微镜下精准勾勒出心脏内部结构的轮廓。- Alcam(活化白细胞粘附分子) :通过免疫组化染色标记 Alcam,可以特异性地显现出构成瓣叶的内皮细胞以及心肌细胞膜,从而清晰分辨出瓣膜的精细结构。
- DAF-FMDA (DAF) :这种荧光探针被用来标记围绕在流出道(OFT)区域的血管平滑肌细胞,帮助研究者观察瓣膜周边的组织环境。
- BODIPY 神经酰胺 (BODIPY ceramide) :在活体成像中,使用这种染料可以清晰地勾勒出发育中的瓣膜瓣叶边缘。
多基因风险评分 (PRS) 与全表型组关联分析 (PheWAS)
研究方法:使用 LDpred2 算法开发了 PRS,在独立队列(QUEBEC-BAV)中验证其预测能力,并在 UK Biobank 数据库中针对 976 种表型进行全表型组关联分析 (PheWAS) 。
研究结果:PRS 与 BAV 风险高度相关(每增加一个标准差,患病风险增加 2.07 倍)。此外,高 PRS 还显著增加了胸主动脉瘤、主动脉瓣狭窄以及心房颤动的患病风险。
虽然回归分析通常只代表相关性,但 PRS 具有一定的特殊性,使其在解释上比一般的观察性研究更接近因果链条:
- 先天性:由于 PRS 是基于个体出生时就确定的遗传变异计算的,它不存在“因果倒置”的问题(即不是因为得了心脏病才改变了基因)。
- 多效性 (Pleiotropy) :PheWAS 的结果更多地揭示了基因多效性,即同样的遗传基础可能同时参与了瓣膜发育和其他心血管疾病的发生过程。
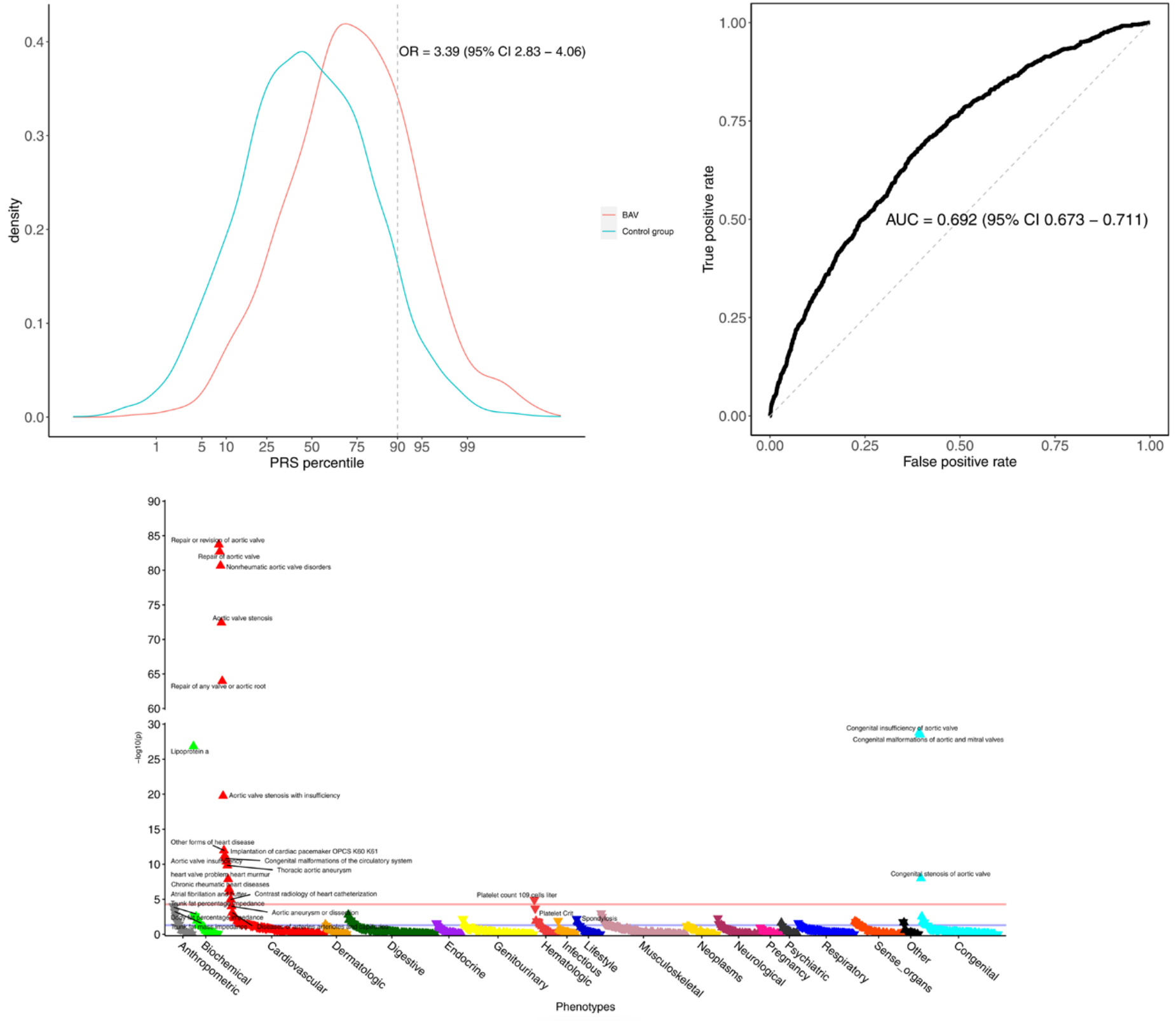
- Figure 6 展示了 PRS 在病例和对照中的分布、预测 BAV 的 ROC 曲线,以及 PRS 与多种心血管表型关联的 PheWAS 结果图。
- 逻辑梳理:6A 证明患者和健康人的遗传风险确实不同;6B 量化了这种区分有多准;6C 则告诉我们,高风险人群不仅要担心 BAV,还要防范主动脉瘤和房颤等并发症。
BAV全基因组显著性位点对照表(GAWS)
根据文章中的研究结果,以下是本次全基因组关联分析(GWAS)元分析中识别出的 36 个全基因组显著性位点(Loci) 的详细数据汇总表:
BAV 全基因组显著性位点对照表
| 编号 (Locus) | 变异位点 (rsID) | 染色体 (Chr) | 位置 (Pos) | 风险/非风险等位基因 (RA/NRA) | 风险等位基因频率 (RAF) | 比值比 (OR [95% CI]) | P 值 (P Value) | 最近基因 (Gene) | 是否新发现 (Novel) |
|---|---|---|---|---|---|---|---|---|---|
| 1 | rs116386356 | 1 | 22262631 | C/T | 0.069 | 1.29 (1.21–1.37) | 2.57E-14 | WNT4 | Yes |
| 2 | rs11166276 | 1 | 99579683 | T/C | 0.495 | 1.35 (1.30–1.39) | 3.52E-60 | PALMD | No |
| 3 | rs926521 | 1 | 167623295 | T/C | 0.451 | 1.12 (1.08–1.16) | 8.39E-11 | RCSD1 | Yes |
| 4 | rs2761557 | 1 | 183610464 | C/T | 0.642 | 1.11 (1.07–1.15) | 4.64E-09 | ARPC5 | Yes |
| 5 | rs62132550 | 2 | 36913942 | C/T | 0.560 | 1.14 (1.10–1.18) | 1.08E-13 | STRN | Yes |
| 6 | rs12613022 | 2 | 40346783 | G/A | 0.629 | 1.11 (1.07–1.15) | 5.51E-09 | SLC8A1 | Yes |
| 7 | rs6715876 | 2 | 65259794 | C/T | 0.367 | 1.14 (1.10–1.18) | 5.43E-14 | ACTR2 | Yes |
| 8 | rs7593336 | 2 | 145078862 | G/A | 0.427 | 1.14 (1.10–1.18) | 1.51E-13 | ZEB2 | No |
| 9 | rs1505373 | 2 | 212377960 | C/T | 0.585 | 1.10 (1.06–1.14) | 4.33E-08 | ERBB4 | Yes |
| 10 | rs11128363 | 3 | 73695511 | C/A | 0.739 | 1.18 (1.13–1.23) | 2.12E-14 | PDZRN3 | Yes |
| 11 | rs1706003 | 3 | 194579238 | G/T | 0.569 | 1.17 (1.12–1.22) | 3.79E-13 | TMEM44 | Yes |
| 12 | rs2246771 | 3 | 195760866 | A/G | 0.340 | 1.22 (1.18–1.27) | 3.75E-26 | MUC4 | No |
| 13 | rs12502542 | 4 | 108216398 | G/A | 0.582 | 1.16 (1.12–1.20) | 4.82E-17 | LEF1 | Yes |
| 14 | rs10034133 | 4 | 125788461 | C/T | 0.455 | 1.10 (1.07–1.14) | 2.07E-08 | FAT4 | Yes |
| 15 | rs114728151 | 4 | 139740573 | C/T | 0.927 | 1.30 (1.21–1.39) | 1.23E-14 | MGST2/MAML3 | Yes |
| 16 | rs7676725 | 4 | 168739540 | A/G | 0.494 | 1.14 (1.10–1.18) | 2.26E-14 | PALLD | Yes |
| 17 | rs67041063 | 5 | 32617685 | A/G | 0.708 | 1.12 (1.08–1.16) | 5.65E-09 | SUB1 | Yes |
| 18 | rs4869594 | 5 | 38731246 | A/C | 0.390 | 1.14 (1.10–1.18) | 6.35E-14 | OSMR | Yes |
| 19 | rs58547370 | 5 | 82373029 | A/G | 0.108 | 1.17 (1.11–1.23) | 2.27E-08 | RPS23 | Yes |
| 20 | rs57256120 | 5 | 123168317 | G/A | 0.289 | 1.12 (1.08–1.16) | 2.03E-09 | PRDM6 | Yes |
| 21 | rs9378715 | 6 | 2573580 | G/A | 0.271 | 1.12 (1.08–1.16) | 9.76E-09 | MYLK4 | Yes |
| 22 | rs11751669 | 6 | 22570808 | A/G | 0.730 | 1.13 (1.09–1.18) | 7.68E-11 | HDGFL1 | Yes |
| 23 | rs62430519 | 6 | 142273695 | C/T | 0.305 | 1.15 (1.10–1.20) | 8.40E-11 | VTA1 | Yes |
| 24 | rs118039278 | 6 | 160564494 | A/G | 0.068 | 1.21 (1.13–1.29) | 1.94E-08 | LPA | Yes |
| 25 | rs118065347 | 8 | 11942355 | G/A | 0.044 | 1.59 (1.47–1.73) | 7.19E-30 | DEFB136 | No |
| 26 | rs1755290 | 9 | 17939172 | T/C | 0.597 | 1.16 (1.12–1.20) | 5.68E-16 | ADAMTSL1 | Yes |
| 27 | rs10878881 | 12 | 68960853 | C/T | 0.649 | 1.11 (1.07–1.15) | 1.12E-08 | CPM | Yes |
| 28 | rs7307097 | 12 | 89946230 | G/A | 0.746 | 1.15 (1.10–1.20) | 4.68E-09 | ATP2B1 | Yes |
| 29 | rs567223 | 12 | 114672766 | G/T | 0.483 | 1.12 (1.08–1.16) | 4.03E-09 | TBX3 | Yes |
| 30 | rs9506819 | 13 | 22286130 | T/G | 0.421 | 1.13 (1.09–1.16) | 3.44E-12 | FGF9 | Yes |
| 31 | rs735722 | 13 | 104571923 | T/C | 0.287 | 1.19 (1.15–1.24) | 3.24E-21 | DAOA | Yes |
| 32 | rs759283 | 14 | 72889599 | A/C | 0.340 | 1.12 (1.09–1.16) | 7.26E-11 | DPF3 | Yes |
| 33 | rs9960148 | 18 | 25837395 | G/T | 0.625 | 1.12 (1.08–1.16) | 1.01E-10 | SS18 | Yes |
| 34 | rs3185010 | 19 | 11165166 | G/A | 0.684 | 1.13 (1.09–1.17) | 2.70E-10 | KANK2 | Yes |
| 35 | rs574693724 | 20 | 57443143 | C/CG | 0.421 | 1.14 (1.09–1.20) | 2.76E-09 | RBM38 | Yes |
| 36 | rs117651913 | 22 | 42854060 | T/A | 0.017 | 1.60 (1.36–1.89) | 3.05E-08 | ARFGAP3 | Yes |
数据说明:
- Pos (Position) :基于 GRCh38 人类基因组坐标。
- RA/NRA (Risk/Non-risk Allele) :风险等位基因/非风险等位基因。
- RAF (Risk Allele Frequency) :风险等位基因在群体中的频率。
- OR (Odds Ratio) :风险每增加一个等位基因的关联强度;大于 1 表示增加风险。
- Gene:该位点物理位置上最近的蛋白质编码基因。加粗字体表示该基因也通过了“SNP-to-gene”综合策略的优先排序。
- Novel:“Yes”代表本次研究首次发现的新位点(共 32 个),“No”代表此前已被报道过的已知位点(共 4 个)。
讨论
核心研究结果
本研究的三大突破:通过大规模 GWAS 识别了 36 个基因组位点(其中 32 个为首次发现);利用转录组数据和斑马鱼模型优先排序并验证了候选致病基因;并首次开发了与 BAV 稳健相关的 PRS(多基因风险评分) 。
核心致病基因的分子机制解析
作者对最具代表性的候选基因进行了详细的功能解读:
- 肌动蛋白(Actin)调节相关基因:重点分析了 KANK2,指出其作为肌动蛋白聚合调节因子影响细胞迁移,并在斑马鱼中通过增加内皮细胞数量验证了其在瓣叶发育中的作用。同时也提到了相关基因 ERBB4 在瓣膜发生中的已知角色。
- 细胞骨架与平滑肌相关基因:探讨了 STRN(参与细胞骨架组织)和 PRDM6(调节血管平滑肌细胞)的作用。研究强调 STRN 缺失会导致斑马鱼流出道(OFT)缩短及瓣膜缺陷。
- Wnt 信号通路:深入讨论了该通路中的核心基因 LEF1 和 WNT4,它们在瓣膜发育的间充质转化过程中具有关键地位,且在斑马鱼实验中均表现出显著的瓣膜畸形表型。
GWAS 信号的多效性与关联性分析
作者进一步探讨了 BAV 与其他心血管疾病的遗传重叠:
- 与 CAVS(钙化性主动脉瓣狭窄)的联系:指出虽然大多数位点是 BAV 特有的,但部分位点(如 LPA 、PALMD**)与 CAVS 存在共同遗传基础,暗示了 BAV 与瓣膜退行性变之间复杂的交织关系。
- 超越显著位点的发现:讨论了位于 GWAS 显著位点之外、但在转录组分析中具有因果证据的基因,如 CSK 、NNT** 和 FES,展示了跨组织分析的补充作用。
遗传架构的宏观思考:单基因 vs 多基因
作者对比了单基因突变与常见变异的作用:
- 多基因贡献:指出 BAV 并非仅由少数罕见突变(如 GATA4)引起,更多是由具有微小效应的多基因共同作用导致的。
- PRS 的临床潜力:强调 PRS 在识别高风险人群及预测主动脉瘤、房颤等并发症方面的优异表现(OR=2.07),其预测效力甚至超过了某些复杂性状。
研究局限性与未来展望
- 样本偏差:手术队列可能更偏向于有并发症的患者。
- 族裔局限:分析仅限于欧洲裔,结果在其他族裔中的通用性有待验证。
- 机制深化:指出未来仍需要更多功能研究来阐明这些基因在发育中的精确逻辑。
总结
全文最后总结:BAV 具有显著的多基因起源,其发育障碍源于心脏胚胎发育相关通路中多个常见变异的累积效应。
个人启发
- 传统的瓣膜研究往往局限于瓣膜组织本身,但本文证明 BAV 的致病基因可能在邻近组织中通过遗传调控发挥作用。那么瓣膜钙化是否也会收到临近组织的调控?在寻找瓣膜病病因时,可以尝试将视角扩大到“左心室-主动脉-瓣膜”这一发育功能单元。例如,研究发现 STRN 在左心室中的表达变化与 BAV 相关,而 PRDM6 的风险信号则在主动脉组织中最为显著。这意味着某些瓣膜畸形可能是心脏流出道整体形态发生障碍的局部表现。
- 过去的研究多聚焦于瓣膜钙化,而本文识别出许多细胞骨架的物理结构调控。文中 KANK2、ACTR2 和 ARPC5 均涉及肌动蛋白(Actin)聚合及细胞迁移功能。这提示我们,瓣膜发育异常可能源于早期内皮细胞迁移的“步态”失稳。后续可以深入探讨机械力传导及细胞骨架动态平衡在瓣膜形态维持中的交互作用。
- 在后续研究中尝试利用大样本的基因组数据提升论证的可靠性。
-–
BAV与CAVD相关GWAS研究综述( AI生成 截至2026-03-01)
Executive Summary
- BAV/CAVD(含AS/AVC)遗传学证据已经从“单个位点发现”进入“多位点+多组学+功能验证”阶段。
- 最稳健、跨研究重复度最高的信号是
LPA/Lp(a)轴(最早从AVC到AS结局均见一致)[1][2][5]。 PALMD是另一条高度重复的主线(AS与CAVS均可复现,并有阀组织表达证据)[2][3][5]。- 近两年大样本研究显著扩展位点数量(AS可达数百位点),但“表型异质性(BAV/CAVS/AS/AVC定义不一)+祖源不平衡”仍是主要解释瓶颈[6][8][9]。
- BAV方面,2017年
GATA4为早期代表,2026年大样本GWAS显示明显多基因架构并提供斑马鱼验证,但跨人群外推仍需更多独立复现[4][10]。
Key Findings(关键研究表)
| 研究 | 表型 | 样本量 | 关键位点/基因 | 机制/功能证据 |
|---|---|---|---|---|
| Thanassoulis 2013 | AVC/AS | AVC 6942;MAC 3795 | LPA | Lp(a)因果线索,跨人群复现 |
| Helgadottir 2018 | AS | 2457病例+349342对照(后续扩展) | PALMD/TEX41/LPA | 发育与动脉粥样硬化通路并存 |
| Thériault 2018 | CAVS | 1009病例/1017对照 + UKB复现 | PALMD | TWAS+阀组织eQTL支持 |
| Small 2023 (MVP) | CAS/AS | 14451病例/398544对照 | PALMD/TEX41/IL6/LPA/FADS | 多祖源分析;LDL效应受Lp(a)影响 |
| Thériault 2024 | CAVS | 14819病例/941863参与者 | 32位点(20新) | 阀RNA-seq + TWAS/共定位/MR |
| Thériault 2026 | BAV | 9631病例/65677参与者 | 36位点(32新) | 斑马鱼验证WNT4/LEF1/STRN/KANK2 |
References
[1] Genetic associations with valvular calcification and aortic stenosis | N Engl J Med / PubMed | 2013-02-07
[2] Genome-wide analysis yields new loci associating with aortic valve stenosis | Nature Communications / PubMed | 2018-03-07
[3] A transcriptome-wide association study identifies PALMD as a susceptibility gene for calcific aortic valve stenosis | Nature Communications / PubMed | 2018-03-07
[4] Protein-altering and regulatory genetic variants near GATA4 implicated in bicuspid aortic valve | Nature Communications / PubMed | 2017-05-25
[5] Multiancestry Genome-Wide Association Study of Aortic Stenosis Identifies Multiple Novel Loci in the Million Veteran Program | Circulation / PubMed | 2023-03-21
[6] Integrative genomic analyses identify candidate causal genes for calcific aortic valve stenosis involving tissue-specific regulation | Nature Communications / PubMed | 2024-03-18
[7] Distinct Genetic Risk Profile in Aortic Stenosis Compared With Coronary Artery Disease | JAMA Cardiology | 2025-02-01
[8] Multitrait analyses identify genetic variants associated with aortic valve function and aortic stenosis risk | Nature Genetics / PubMed | 2025-12-19 (online)
[9] Genomic and transcriptomic analyses of aortic stenosis enhance therapeutic target discovery and disease prediction | Nature Genetics / PubMed | 2025-12-19 (online)
[10] Genome and Transcriptome-Wide Analyses Identify Multiple Candidate Genes and a Significant Polygenic Contribution in Bicuspid Aortic Valve | Circulation / PubMed | 2026-02-06
[11] Multipopulation Genome-Wide Association Study Identifies Novel Loci for Bicuspid Aortic Valve and Reveals Shared Genetic Architecture With Aortopathies | Circ Genom Precis Med / PubMed | 2025-11-08 (online ahead of print)






暂无评论内容